- Microsoft student con encarta premiun 2008
- monografias.com
- es.wikipedia.org
- colegiocolon.edu.co
BIBLIOGRAFIA
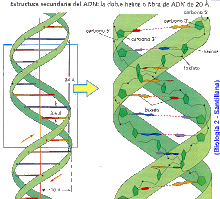
REPLICACIÓN DEL ADN EN EUCARIOTAS Y PROCARIOTAS
Replicación en procariontes.
Ocurre en tres etapas:
1ª etapa: desenrrollamiento y apertura de la doble hélice.en el punto ori.
En el punto de origen u ORI, que es un lugar del cromosoma con gran contenido de A y T, la doble hélice se abre, mediante la DNA helicasa y las proteínas desestabilizadoras de la hélice o proteínas de unión a DNA de una sola cadena, vuelven recta la cromatina y la mantienen abierta. La DNA polimerasa sintetiza las cadenas complementarias a cada una de las cadenas primitivas. Forma dos copias activas de ADN, una es continua, o sea, basta con agregar los nucleotidos correspondientes porque la hebra antigua tiene 3', por lo que se crea una 5´. En la otra hebra, se produce un proceso discontinuo, debido a que la hebra quedo con un final 5', debiendo partir con un 3', y la célula es incapaz de seguir la cadena con este final, para que se inicie la copia del DNA hace falta un corto RNA específico (10 pares de bases), denominado RNA cebador, que hace que empiece a actuar la DNA polimerasa. El RNA cebador es generado por la RNA primasa (sintetizadora de RNA). Esta enzima se une directamente a la DNA helicasa, formando un complejo llamada primosoma, que se va desplazando con la cadena en formación. Conforme van existiendo fragmentos de cadena abiertos de suficiente longitud, se va sintetizando la cadena discontinua formando pequeños fragmentos, denominados Fragmentos de Okazaki, cada uno de unos 1000 nucleótidos. . Hace falta un RNA cebador por cada fragmento de Okazaki. La RNA primasa, va sintezando a intervalos los RNA cebadores que van siendo incorporados a la copia como si fueran ADN, entre los fragmentos de Okazaki, hasta que se alcanza el RNA cebador del fragmento de Okazaki ya terminado. . La cadena con ARN cebador, es denominada cadena retrasada
El DNA sintetizado en la cadena retrasada y su cadena patrón sufren un plegamiento, de tal forma que la DNA polimerasa de la cadena conductora se unen para formar un complejo único, de modo que las proteínas de replicación puedan utilizarse conjuntamente en la replicación de ambas cadenas. Las topoisomerasas mantienen esta estructura y evitan que el DNA se enrede por superenrrollamiento, cortando un enlace fosfodiester, y a esto se le llama nick.Además, existe una proteína llamada SSB, que estabiliza la forma monocatenaria de la hebra en replicación, para que no se acople por complementariedad de bases con ella misma.
Las enzimas ligasas son las encargadas, despues, de ir arreglando los nicks cuando se sustituye el ARN cebador.
Exiten tres tipos de ADN-polimerasa, la I, es la encarga de reparar la hebra; la II, de ayudar a la III; y la III, agrega las bases a la hebra.
La labor de la ADN-pol I es exonucleasa, puede poner bases como sacar bases, con esto puede reparar la hebra. El dominio de esta proteína encargado de incluir bases a la hebra se llama Fragmento Klenow, que puede ser liberado del resto de la proteína por la Tripsina.
DUPLICACIÓN DEL ADN EN EUCARIONTES
Es similar a la de los procariontes, es decir, semiconservativa y bidireccional. Existe una hebra conductora y una hebra retrasada con fragmentos de Okazaki. Se inicia en ORI (puede haber unas 100 a la vez), entre las diferencia, se comienza con las polimerasas, son más complejas, y además, la polimerasa de la hebra continua es diferente a la de la hebra discontinua. De la hebra continua se encarga la polimerasa Delta y de la discontinua, la Alfa.
Las helicasa difieren en estructura, las primasas se encuentran adosadas a la ADN-pol Alfa.
El resto del proceso es muy parecido.
En el final de la hebra antigua que da la base a la hebra discontinua, queda una zona denominada telómero, que no tiene como obtener su dupla en la hebra discontinua, debido a que no es posible insertar un nuevo ARN cebador, ni mucho menos un fragmento de Okazaki. Al no tener su par, son eliminados automáticamente, perdiendose. Existen enzimas, las telomerasas, que repiten esta secuencia varias veces, cosa que no se pierda información esencial del genoma. Las enzimas encargadas de cortar el telómero, son las topoisomerasas 4.
El ARN cebador es retirado por el complejo de reparación de la célula.
COMO SE DA EL PROCESO DE REPLICACIÓN
El proceso se puede dividir en 3 fases: iniciación, elongación y terminación.
Iniciación
Para que pueda formarse la horquilla de replicación es necesario que las dos cadenas se separen para sintetizar el cebador y el ADN de la cadena de nueva síntesis. Para ello el ADN debe desenrollarse y el punto de partida viene determinado por una secuencia específica de nucleótidos conocida como origen de replicación; en E. coli, el origen de replicación se conoce como oriC. Esta secuencia contiene gran cantidad de adenina y timina, lo que facilita la separación de las cadenas, y es reconocida por proteínas iniciadoras que controlan este proceso, de forma que una vez unidas las proteínas iniciadoras al ADN provocan el desenrollamiento de estas regiones de fácil desnaturalización.
A continuación las proteínas iniciadoras reclutan el resto de proteínas que conforman el replisoma y que son necesarias para la síntesis de ARN y ADN, empezando por la helicasa (o topoisomerasa II). Esta enzima, generalmente con forma de anillo y de alta procesividad, se une a la región de ADN monocatenario resultante del desenrollamiento, desplazándose a lo largo del ADN mediante consumo de ATP en dirección a la horquilla de replicación, es decir, en dirección 5' → 3' en la hebra rezagada y 3' → 5' en la hebra adelantada, rompiendo los puentes de hidrógeno que mantienen unida la doble hélice. El siguiente conjunto de proteínas reclutadas son las denominadas proteínas SSB (single-stranded DNA binding proteins, proteínas ligantes de DNA monocatenario) encargadas de la estabilización del ADN monocatenario generado por la acción de las helicasas, impidiendo así que el ADN se renaturalice o forme de nuevo la doble hélice, de manera que pueda servir de molde. Estas proteínas se unen de forma cooperativa, por lo que su unión al DNA conforme avanza la helicasa es rápida. Por otro lado, conforme las helicasas van avanzando se van generando superenrollamientos en la doble cadena de ADN por delante de la horquilla y si éstos no fueran eliminados, llegado a un punto lel replisoma ya no podría seguir avanzando. Las topoisomerasas son las enzimas encargadas de eliminar los superenrollamientos cortando una o las dos cadenas de ADN y pasándolas a través de la rotura realizada, sellando a continuación la brecha.
Elongación
En el siguiente paso, la holoenzima ADN Pol III cataliza la síntesis de las nuevas cadenas añadiendo nucleótidos sobre el molde. Esta síntesis se da bidireccionalmente desde cada origen, con dos horquillas de replicación que avanzan en sentido opuesto. Cuando el avance de dos horquillas adyacentes las lleva a encontrarse, es decir, cuando dos burbujas se tocan, se fusionan, y cuando todas se han fusionado todo el cromosoma ha quedado replicado.
Puesto que la holoenzima ADN Pol III necesita de un extremo 3'-OH libre, es necesario que una ARN primasa catalice la formación de un fragmento corto específico de ARN llamado cebador, que determinará el punto por donde la ADN polimerasa comienza a añadir nucleótidos. Así, durante la síntesis, en cada horquilla de replicación se van formando dos copias nuevas a partir del cebador sintetizado en cada una de las dos hebras de ADN que se separaron en la fase de iniciación, pero debido a la unidireccionalidad de la actividad polimerasa de la ADN Pol III, que sólo es capaz de sintetizar en sentido 5´ → 3', la replicación sólo puede ser continua en la hebra adelantada; en la hebra rezagada es discontinua, dando lugar a los fragmentos de Okazaki).
La mitad del dímero de la holoenzima ADN Pol III sintetiza la hebra adelantada y la otra mitad la hebra rezagada.
En la hebra rezagada, cuando la ADN Pol III hace contacto con el extremo de otro fragmento de Okazaki contiguo, el cebador de ARN de éste es eliminado y los dos fragmentos de Okazaki de ADN recién sintetizado son unidos. Una vez se han juntado todos se completa la doble hélice de ADN. La eliminación de cebadores también se da en la hebra conductora, de síntesis continua, pero debido a que en ésta hay un solo cebador es un proceso que sólo tiene lugar una vez, mientras que en la hebra rezagada se dará tantas veces como fragmentos de Okazaki haya. Para ello intervienen una serie de enzimas: la enzima RNasa H ("H" de híbrido ARN-ADN) elimina el cebador a excepción del ribonucleótido directamente unido al ADN; la ADN Pol I elimina este ribonucleótido gracias a su actividad exonucleasa 5' → 3' y rellena el hueco con ADN quedando una molécula completa a excepción de una rotura (o "mella") entre el extremo 3'-OH libre y el fosfato 5' de la cadena reparada; por último, la ADN ligasa sella esa rotura catalizando la reacción de condensación entre el grupo fosfato y el OH de la desoxirribosa del nucleótido contiguo, completando el enlace fosfodiéster; para ello, es preciso hidrolizar una molécula de ATP.
Terminación
Al finalizar la síntesis de ARNm, esta molécula ya se ha separado completamente del ADN (que recupera su forma original) y también de la ARN polimerasa, terminando la transcripción. La terminación es otra etapa distinta de la transcripción, porque justo cuando el complejo de transcripción se ha ensamblado activamente debe desensamblarse una vez que la elongación se ha completado. La terminación está señalizada por la información contenida en sitios de la secuencia del ADN que se está transcribiendo, por lo que la ARN polimerasa se detiene al transcribir algunas secuencias especiales del ADN. Estas secuencias son ricas en guanina y citosina, situadadas en el extremo de los genes, seguidas de secuencias ricas en timina, formando secuencias palindrómicas, que cuando se transcriben el ARN recién sintetizado adopta una estructura en horquilla que desestabiliza el complejo ARN-ADN, obligando a separarse de la ARN polimerasa, renaturalizándose la burbuja de transcripción. Algunas secuencias de ADN carecen de la secuencia de terminación, sino que poseen otra secuencia a la que se unen una serie de proteínas reguladoras específicas de la terminación de la transcripción como rho .
REPLICACIÓN DE ADN
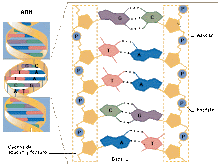
El proceso de replicación de ADN es el mecanismo que permite al ADN duplicarse (es decir, sintetizar una copia idéntica). Esta duplicación del material genético se produce de acuerdo con un mecanismo semiconservador, lo que indica que las dos cadenas complementarias del ADN original, al separarse, sirven de molde cada una para la síntesis de una nueva cadena complementaria de la cadena molde, de forma que cada nueva doble hélice contiene una de las cadenas del ADN original. Gracias a la complementariedad entre las bases que forman la secuencia de cada una de las cadenas, el ADN tiene la importante propiedad de reproducirse idénticamente, lo que permite que la información genética se transmita de una célula madre a las células hijas y es la base de la herencia del material genético.
La molécula de ADN se abre como una cremallera por ruptura de los puentes de hidrógeno entre las bases complementarias liberándose dos hebras y la ADN polimerasa sintetiza la mitad complementaria añadiendo nucleótidos que se encuentran dispersos en el núcleo. De esta forma, cada nueva molécula es idéntica a la molécula de ADN inicial.
La replicación empieza en puntos determinados: los orígenes de replicación. Las proteínas iniciadoras reconocen secuencias de nucleótidos específicas en esos puntos y facilitan la fijación de otras proteínas que permitirán la separación de las dos hebras de ADN formándose una horquilla de replicación. Un gran número de enzimas y proteínas intervienen en el mecanismo molecular de la replicación, formando el llamado complejo de replicación o replisoma. Estas proteínas y enzimas son homólogas en eucariotas y arqueas, pero difieren en bacterias.